Mimétisme moléculaire: un lien direct entre réplication de l'ADN et maintenance épigénétique
Une collaboration internationale menée par Pierre-Antoine Defossez au Centre épigénétique et destin cellulaire, dévoile un nouveau phénomène de mimétisme moléculaire qui lie deux processus cellulaires fondamentaux: la réplication de l'ADN, et le maintien de l'information épigénétique. Ces travaux font progresser la connaissance des mécanismes épigénétiques et ouvrent des perspectives nouvelles pour le développement de molécules d'intérêt thérapeutique. Cette étude a été publiée le 4 août 2017 dans la revue Molecular Cell.
Nos chromosomes portent deux types d'information: l'information génétique, déterminée par la séquence des nucléotides, et l'information épigénétique. Cette dernière est un élément fondamental de l'identité des cellules; elle se superpose à la séquence sans la modifier, et elle marque notamment les régions exprimées ou silencieuses. Une des marques épigénétiques essentielles est la méthylation de l'ADN.
A chaque cycle cellulaire, l'ADN est répliqué, et les nouveaux brins sont initialement vierges de méthylation. Il faut donc y reproduire, de façon fidèle, le patron de méthylation porté par les brins d'ADN parentaux.
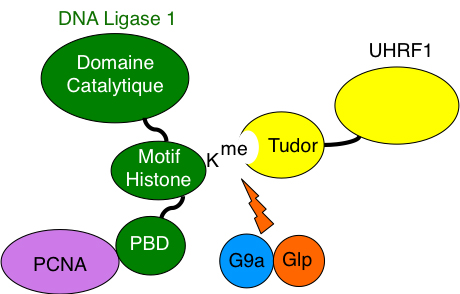
Une molécule cruciale dans ce processus est la protéine UHRF1: en son absence, le processus de reméthylation de l'ADN est profondément perturbé. Une question importante mais non résolue, toutefois, est de déterminer comment la protéine UHRF1 "trouve" les régions de l'ADN en réplication pour y exercer son action. En effet, UHRF1 est connue pour lier certaines protéines histones qui structurent l'ADN, sont très abondantes, et peu mobiles. Dans ces conditions, comment UHRF1 acquiert-elle la mobilité et la spécificité nécessaires à la reconnaissance de l'ADN en réplication?
Le travail publié par Ferry et al. répond à cette question. La collaboration entre l'équipe française et ses partenaires japonais, allemands, et américains met de fait en évidence un nouveau mécanisme liant réplication de l'ADN et méthylation de l'ADN. Dans un exemple de mimétisme moléculaire surprenant, une des enzymes de réplication présente en effet un domaine ressemblant aux histones, à tel point qu'il est même la cible d'enzymes normalement spécialisées dans le marquage des histones. La protéine UHRF1 se fixe très avidement à ce motif pseudo-histone, ce qui assure son recrutement au niveau des zones en réplication, et la méthylation de l'ADN correspondant.
Les expériences fonctionnelles, utilisant des cellules souches murines modifiées finement par une approche CRISPR/Cas9, montrent que ce nouveau mécanisme est crucial pour le maintien de l'information épigénétique, et donc pour l'identité des cellules.
Ces travaux ouvrent la possibilité de chercher à produire des molécules interférant avec le mécanisme découvert, et qui auraient pour effet de diminuer la méthylation de l’ADN. De telles molécules pourraient ensuite être testées pour leur activité anticancéreuse, car de nombreux cancers dépendent de façon critique de la méthylation de l’ADN.
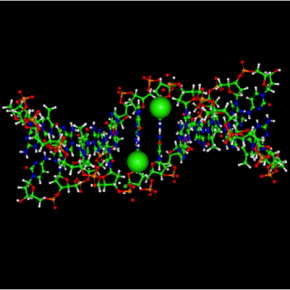
Figure 1 : La méthylation de l’ADN. Modèle moléculaire de la double hélice, incluant deux cytosines méthylées; l’espace occupé par leurs groupements CH3 est représenté par une sphère verte. On peut noter comment ces groupements se font face et sont positionnés dans le grand sillon.
© Pierre-Antoine Defossez
© Pierre-Antoine Defossez
En savoir plus
-
Methylation of DNA Ligase 1 by G9a/GLP Recruits UHRF1 to Replicating DNA and Regulates DNA Methylation.
Ferry L, Fournier A, Tsusaka T, Adelmant G, Shimazu T, Matano S, Kirsh O, Amouroux R, Dohmae N, Suzuki T, Filion GJ, Deng W, de Dieuleveult M, Fritsch L, Kudithipudi S, Jeltsch A, Leonhardt H, Hajkova P, Marto JA, Arita K, Shinkai Y, Defossez PA.
Mol Cell. 2017 Aug 4. pii: S1097-2765(17)30506-3. doi: 10.1016/j.molcel.2017.07.012