Orchestration de la dynamique tridimensionnelle des chromosomes lors du cycle cellulaire
A chaque division cellulaire, le patrimoine génétique contenu dans les chromosomes doit être dupliqué et ségrégé dans les cellules filles. Ces processus sont accompagnés de modifications structurales, régulées par des protéines conservées chez la plupart des organismes vivants. Des chercheurs de l’équipe Régulation spatiale des génomes à l’Institut Pasteur et du laboratoire de Physique théorique de la matière condensée à l’Université P. et M. Curie, ont suivi les transitions structurales des 16 chromosomes du génome de levure au cours du cycle cellulaire en étudiant leur organisation tridimensionnelle dans des populations synchronisées et/ou mutantes. Cette étude qui révèle en outre un possible nouveau mécanisme facilitant la ségrégation des chromosomes, a été publiée le 20 juillet 2017 dans la revue EMBO Journal.
La duplication et la ségrégation des chromosomes impliquent une réorganisation dynamique de leur structure par les complexes protéiques de maintenance de la structure des chromosomes (SMC), conservés chez les eucaryotes comme chez les procaryotes. Les chercheurs ont réussi à suivre ces changements structuraux à l’échelle du génome en utilisant la capture de conformation de chromosomes (Hi-C) sur des populations de cellules préalablement synchronisées. Cette technique consiste à « geler », grâce à un agent fixateur, les structures 3D de tous les ADN présents dans chaque noyau. Les fréquences de contacts entre toutes les positions le long de ces molécules d’ADN sont alors quantifiées par séquençage haut débit. Une carte de contacts entre toutes les positions d’un génome peut alors être générée, reflétant la structure 3D moyenne des chromosomes dans la condition étudiée. En utilisant des mutants, les chercheurs ont ainsi pu observer, à l’échelle du génome, le rôle des SMC dans la réorganisation structurelle de ce dernier au cours du cycle.
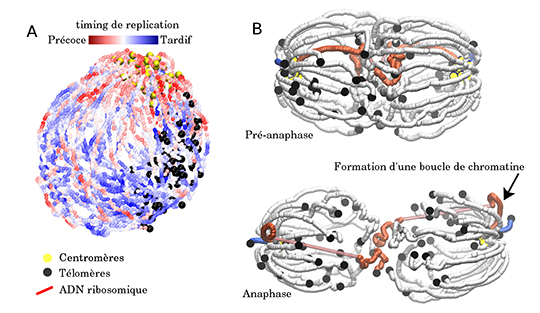
Durant la réplication, un chromosome est dupliqué en deux chromatides sœurs. En combinant les structures Hi-C au profil temporel de réplication, les chercheurs ont pu générer pour la première fois une carte de réplication tridimensionnelle qui illustre le programme spatio-temporel de duplication du génome. La structure obtenue montre l’établissement dans l’espace nucléaire d’une vague coordonnée de réplication, débutant au niveau des centromères co-localisés pour finir, plus tardivement, au niveau des télomères (Fig. A). Lors de la réplication, les chromatides sœurs demeurent appariées et sont condensées par le complexe SMC cohésine, ce qui conduit à l’individualisation des chromosomes les uns par rapport aux autres. A la suite de la réplication, les cellules entrent en mitose et se divisent. Les chromosomes lors de cette phase sont séparés par des forces mécaniques exercées par les microtubules du fuseau mitotique. La synchronisation des cellules en anaphase, lorsque les chromatides sœurs sont séparées dans les deux cellules filles, a révélé des chromosomes sous une tension due aux forces mécaniques générées notamment par le faisceau de microtubules. De plus, les contacts ont mis en évidence une boucle de chromatine reliant les centromères des chromosomes et le locus contenant les gènes codant les ribosomes qui se trouvent au milieu du grand bras du chromosome 12. Cette boucle de chromatine est dépendante de l’action des SMC condensines, et suggère que ce complexe, jusqu’alors connu pour faciliter la condensation des chromatides sœurs individualisées, pourrait ainsi participer plus activement à la ségrégation de certains chromosomes, en soutien à l’action du faisceau de microtubules (Fig B).
© Romain Koszul, Julien Mozziconacci
En savoir plus
-
Cohesins and condensins orchestrate the 4D dynamics of yeast chromosomes during the cell cycle.
Lazar-Stefanita L, Scolari VF, Mercy G, Muller H, Guérin TM, Thierry A, Mozziconacci J, Koszul R. EMBO J. 2017 Jul 20. pii: e201797342. doi: 10.15252/embj.201797342.